Здравствуйте, гость ( Вход | Регистрация )
 2.08.2012 - 14:20 2.08.2012 - 14:20
Сообщение
#1
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
Здравствуйте!
Есть задача определить диагностическую ценность ряда маркеров (допустим, А, В и С) и их комбинаций в диагностике некоторого заболевания. Я расчитал все параметры (чувствительность, специфичность, PPV, NPV, LR) и построил в SPSS ROC-кривые отдельно для А, В и С. Как теперь сделать то же самое для комбинаций этих маркеров, допустим, А+В и В+С? Где копать? Заранее огромное спасибо! |
|
|
 |
 |
 |
Ответов
(1 - 62)
 2.08.2012 - 14:24 2.08.2012 - 14:24
Сообщение
#2
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Здравствуйте! Есть задача определить диагностическую ценность ряда маркеров (допустим, А, В и С) и их комбинаций в диагностике некоторого заболевания. Я расчитал все параметры (чувствительность, специфичность, PPV, NPV, LR) и построил в SPSS ROC-кривые отдельно для А, В и С. Как теперь сделать то же самое для комбинаций этих маркеров, допустим, А+В и В+С? Где копать? Заранее огромное спасибо! можно рандомфорест применить и вклад маркеров по его результатам определить. можно логистическую регрессию для полной модели построить и для комбинаций. модели сравнивать через сравнение ROC.  |
|
|
 |
 |
 2.08.2012 - 14:37 2.08.2012 - 14:37
Сообщение
#3
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
можно рандомфорест применить и вклад маркеров по его результатам определить. можно логистическую регрессию для полной модели построить и для комбинаций. модели сравнивать через сравнение ROC. Big thx за ответ, но я не такой великий спец в статистике - если не затруднит, можно чуть подробнее? Как построить логистическую регрессию для полной модели (как сгруппировать исходные данные?) В идеале - где это все в SPSS и/или Статистике? Ну а если с примером........ Сообщение отредактировал Zaycho - 2.08.2012 - 14:40 |
|
|
 |
 |
 2.08.2012 - 19:38 2.08.2012 - 19:38
Сообщение
#4
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Big thx за ответ, но я не такой великий спец в статистике - если не затруднит, можно чуть подробнее? Как построить логистическую регрессию для полной модели (как сгруппировать исходные данные?) В идеале - где это все в SPSS и/или Статистике? Ну а если с примером........ могу в R показать как понимаю есть эксперимент или наблюдение в котором каждому случаю наличия-отсутствия заболевания соответствует строка наличия-отсутствия признаков? если случаи наблюдения-эксперимента не представляют сочетания наличия-отсутствия признаков то естественно ничего хорошего скорее всего не получится. на такую таблицу (назовем её table) легко натравить randomForest Код rf <- randomForest(Болезнь ~ ., data=table, importance=TRUE, proximity=TRUE) После этого смотрим вклад признаков Код varImpPlot(rf)  |
|
|
 |
 |
 2.08.2012 - 21:55 2.08.2012 - 21:55
Сообщение
#5
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
А можно я все-таки покажу исходные данные?
А, В и С - непрерывные величины Выжил/умер - принимает только 2 значения
Прикрепленные файлы
|
|
|
 |
 |
 3.08.2012 - 08:55 3.08.2012 - 08:55
Сообщение
#6
|
|
|
Группа: Пользователи Сообщений: 116 Регистрация: 20.02.2011 Пользователь №: 23251 |
Здравствуйте! Есть задача определить диагностическую ценность ряда маркеров (допустим, А, В и С) и их комбинаций в диагностике некоторого заболевания. Я расчитал все параметры (чувствительность, специфичность, PPV, NPV, LR) и построил в SPSS ROC-кривые отдельно для А, В и С. Как теперь сделать то же самое для комбинаций этих маркеров, допустим, А+В и В+С? Где копать? Заранее огромное спасибо! Если Вы лучше знакомы с СПСС, постройте модель с помощью логистической регрессии. Заходите в Analyze-Regression-Binary. Факторы А,Б,С перемещаете в Covariates (independent variables), наличие/отсутсвие заболевания в Dependent variable. Закладка Categorical Вам не нужна, поскольку, как я понял, предикторы все у вас количественные. В закладке Save выбираете сохранить вероятности группы (group probabilities). В опциях 95% ДИ, тест Хосмера-Лемешова и все остальное по-желанию. Нажимаете ОК, строится модель, которая включает в себя набор всех предикторов А,Б,С, рассчитанные коэффициенты, р-значения, ДИ и т.д. ROC-кривая строится с помощью меню ROC-curve, где в Test-variable Вы закидываете рассчитанные групповые вероятности, а в State - указываете код, которым у Вас закодировано состояние больного человека (1 например). Построенная логистическая модель может предсказывать аддитивный (суммационный) эффект всех факторов А,Б,С на риск развития заболевания. То есть, все факторы представлены главными эффектами (main effects) - не учитывается возможность взаимодействия фактора А например с фактором Б. Если Вас такое устраивает, можно на этом остановиться. А если Вам интересно посмотреть взаимодействует ли фактор А с фактором Б (присутствует ли синергетический эффект например), нужно построить модель, которая учитывала бы взаимодействие факторов (для этого используется кнопочка a*b в логистической регрессии). Интерпретировать результаты будет намного сложнее, могу посоветовать хорошую книгу на эту тему от Sage publishing - Interaction effects (terms) in logistic regression. Если нравятся случайные леса, установите SPSS Clementine или используйте код, который привел p2004r Сообщение отредактировал TheThing - 3.08.2012 - 08:56 |
|
|
 |
 |
 3.08.2012 - 12:04 3.08.2012 - 12:04
Сообщение
#7
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
А можно я все-таки покажу исходные данные? А, В и С - непрерывные величины Выжил/умер - принимает только 2 значения таблицу чуток пришлось отредактировать от пояснений Код rf<-randomForest(data.na[,2:4],factor(data.na$выжил.умер), proximity=TRUE) > rf Call: randomForest(x = data.na[, 2:4], y = factor(data.na$выжил.умер), proximity = TRUE) Type of random forest: classification Number of trees: 500 No. of variables tried at each split: 1 OOB estimate of error rate: 31.43% Confusion matrix: 0 1 class.error 0 22 11 0.3333333 1 11 26 0.2972973 > round(importance(rf), 2) MeanDecreaseGini A 10.93 B 12.09 C 10.97 > MDSplot(rf, factor(data.na$выжил.умер), k=2, palette=c(1, 2), pch=data.na$выжил.умер) собственно все случаи делятся явно на две группы, и имеются два фактора "выживания". первый фактор действует в обоих группах. второй фактор собственно определяет деление на две группы в одной из которых смертность намного ниже чем во второй группе (и обусловлена действием первого фактора).  |
|
|
 |
 |
 3.08.2012 - 14:27 3.08.2012 - 14:27
Сообщение
#8
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
Огромное спасибо за разъяснения! А можете теперь ткнуть пальцем ламеру, где здесь групповые вероятности, которые можно подставить в ROC-анализ?
Прикрепленные файлы
|
|
|
 |
 |
 3.08.2012 - 14:59 3.08.2012 - 14:59
Сообщение
#9
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Огромное спасибо за разъяснения! А можете теперь ткнуть пальцем ламеру, где здесь групповые вероятности, которые можно подставить в ROC-анализ? для первого датасета Код > data.frame(votes=rf$votes, alive=data.na$выжил.умер, n=data.na$N )
votes.0 votes.1 alive n 1 0.76243094 0.23756906 0 1 2 0.80203046 0.19796954 1 2 3 0.72067039 0.27932961 0 3 4 0.17486339 0.82513661 0 4 5 0.74054054 0.25945946 0 5 6 0.82352941 0.17647059 1 6 7 0.37055838 0.62944162 1 7 8 0.80213904 0.19786096 1 8 9 0.27472527 0.72527473 1 9 10 0.70322581 0.29677419 0 10 11 0.60215054 0.39784946 0 11 12 0.39512195 0.60487805 1 12 13 0.83815029 0.16184971 0 13 14 0.89893617 0.10106383 0 14 15 0.40101523 0.59898477 0 15 16 0.79081633 0.20918367 0 16 17 0.68333333 0.31666667 0 17 18 0.67875648 0.32124352 0 18 19 0.75126904 0.24873096 0 19 20 0.91847826 0.08152174 1 20 21 0.61931818 0.38068182 1 21 22 0.35955056 0.64044944 1 22 23 0.95480226 0.04519774 0 23 24 0.61271676 0.38728324 0 24 25 0.84574468 0.15425532 0 25 26 0.91256831 0.08743169 0 26 27 0.43930636 0.56069364 1 27 28 0.22857143 0.77142857 1 28 29 0.15346535 0.84653465 1 29 31 0.12626263 0.87373737 0 31 33 0.29444444 0.70555556 0 33 34 0.28571429 0.71428571 1 34 35 0.07692308 0.92307692 1 35 36 0.04216867 0.95783133 1 36 37 0.59259259 0.40740741 1 37 38 0.63725490 0.36274510 1 38 39 0.38596491 0.61403509 1 39 40 0.41340782 0.58659218 0 40 41 0.08074534 0.91925466 1 41 42 0.39779006 0.60220994 0 42 43 0.31428571 0.68571429 1 43 44 0.16666667 0.83333333 1 44 45 0.38636364 0.61363636 0 45 46 0.24043716 0.75956284 0 46 47 0.66883117 0.33116883 0 47 48 0.69540230 0.30459770 0 48 49 0.60679612 0.39320388 0 49 50 0.45180723 0.54819277 1 50 51 0.08152174 0.91847826 1 51 52 0.09696970 0.90303030 1 52 53 0.20329670 0.79670330 0 53 54 0.30898876 0.69101124 1 54 55 0.63783784 0.36216216 1 55 56 0.58285714 0.41714286 0 56 57 0.09826590 0.90173410 1 57 58 0.08045977 0.91954023 1 58 59 0.07608696 0.92391304 1 59 60 0.30508475 0.69491525 0 60 61 0.40000000 0.60000000 1 61 62 0.28342246 0.71657754 1 62 63 0.63068182 0.36931818 1 63 64 0.58252427 0.41747573 1 64 65 0.87730061 0.12269939 1 65 66 0.08982036 0.91017964 1 66 67 0.36898396 0.63101604 1 67 68 0.72881356 0.27118644 0 68 69 0.71022727 0.28977273 0 69 70 0.74033149 0.25966851 0 70 71 0.37158470 0.62841530 1 71 72 0.47849462 0.52150538 0 72  |
|
|
 |
 |
 3.08.2012 - 16:05 3.08.2012 - 16:05
Сообщение
#10
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
Глубокоуважаемый p2004r, правильно ли я понял, что первый столбец цифр с большим количеством знаков после запятой - это для А+В, а второй столбец - для В+С?
Если да, то можно то же самое для А+С? СПАСИБО! |
|
|
 |
 |
 3.08.2012 - 16:30 3.08.2012 - 16:30
Сообщение
#11
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Глубокоуважаемый p2004r, правильно ли я понял, что первый столбец цифр с большим количеством знаков после запятой - это для А+В, а второй столбец - для В+С? Если да, то можно то же самое для А+С? СПАСИБО! нет, не так. первые два столбца это вероятность для 0, и вероятность для 1 исхода (они зеркальны). нелинейная модель включает в себя все три исходных фактора. Ваша группа неоднородна. Надо смотреть что из исходных факторов на что влияет. Иными словами --- какой вклад в два фактора про которых я написал в предыдущем посте (группообразующий и повышающий вероятность неблагоприятного исхода).  |
|
|
 |
 |
 3.08.2012 - 16:38 3.08.2012 - 16:38
Сообщение
#12
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
Я вконец запутался. А,В и С - это параметры, не влияющие на наступление исхода. А и В - это результаты биохимических тестов, С - оценка тяжести состояния по интегральной шкале. Все три параметра выше при неблагоприятном исходе. Определенный уровень каждого из них с известной чувствительностью и специфичностью является предиктором неблагоприятного исхода. Нас не устраивает их недостаточная прогностическая ценность по отдельности. Как расчитать эти показатели для комбинаций - я так и не понял...........
|
|
|
 |
 |
 3.08.2012 - 19:29 3.08.2012 - 19:29
Сообщение
#13
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Я вконец запутался. А,В и С - это параметры, не влияющие на наступление исхода. А и В - это результаты биохимических тестов, С - оценка тяжести состояния по интегральной шкале. Все три параметра выше при неблагоприятном исходе. Определенный уровень каждого из них с известной чувствительностью и специфичностью является предиктором неблагоприятного исхода. Нас не устраивает их недостаточная прогностическая ценность по отдельности. Как расчитать эти показатели для комбинаций - я так и не понял........... B имеет несколько больший вес чем A и C. Но сама картина существенно нелинейна. Имеют место две группы --- 1я с более высоким уровнем смертности и низкой прогнозируемостью исхода, и 2я с низким уровнем смертности и визуально более предсказуемым исходом. За разбиение на эти две группы отвечает некая комбинация ABC (её надо проанализировать). В каждой из этих групп действует некий дополнительный фактор определяющий смертность, причем действует количественно разно. Что входит в этот фактор тоже нужно проанализировать. Сначала надо построить решающее правило к какой группе относится конкретный случай, а потом построить для каждой из групп правило исхода.  |
|
|
 |
 |
 3.08.2012 - 20:07 3.08.2012 - 20:07
Сообщение
#14
|
|
|
Группа: Пользователи Сообщений: 116 Регистрация: 20.02.2011 Пользователь №: 23251 |
Согласно моим расчетам лишь фактор С (тяжесть состояния больного) статистически значимо ассоциирован с риском смерти (повышенный риск). Первый столбец цифр - групповые вероятности факторов А+Б+С, второй столбец - вероятности А+Б, третий столбец - А+С, четвертый - Б+С.
0,34015 0,40888 0,34989 0,39730 0,49263 0,50523 0,38566 0,55469 0,42836 0,26548 0,39794 0,62781 0,59121 0,36225 0,60615 0,70132 0,25785 0,31131 0,25945 0,36786 0,43051 0,43519 0,44927 0,47932 0,57229 0,30174 0,58240 0,72457 0,25236 0,38984 0,23751 0,31511 0,48796 0,40442 0,50717 0,56495 0,28626 0,39493 0,29287 0,34319 0,49658 0,37706 0,51123 0,59569 0,37246 0,31495 0,38091 0,50680 0,12237 0,25227 0,11330 0,21316 0,12748 0,31118 0,10785 0,19567 0,53328 0,46286 0,54719 0,57564 0,52075 0,45196 0,49164 0,58775 0,49832 0,42483 0,47445 0,58010 0,36305 0,40782 0,37485 0,42414 0,45776 0,43172 0,47040 0,51505 0,36475 0,42263 0,34469 0,43039 0,57694 0,45255 0,59446 0,62775 0,76129 0,46953 0,75743 0,81078 0,14571 0,39503 0,14859 0,16921 0,13010 0,47251 0,11741 0,13051 0,18435 0,41960 0,15968 0,21998 0,11134 0,39310 0,10980 0,12896 0,86965 0,82693 0,66838 0,83274 0,72274 0,61052 0,74657 0,68379 0,88778 0,82411 0,75763 0,84437 0,86492 0,79245 0,63566 0,81702 0,75099 0,74476 0,35380 0,73615 0,40006 0,19948 0,83108 0,69577 0,83671 0,77659 0,73978 0,64728 0,77173 0,67595 0,67489 0,61222 0,70833 0,62232 0,79319 0,67501 0,82141 0,72640 0,69415 0,70943 0,72958 0,57129 0,70840 0,70052 0,74604 0,59504 0,73655 0,79736 0,77758 0,54065 0,58925 0,63310 0,62808 0,50647 0,55043 0,71285 0,58524 0,40279 0,69639 0,67085 0,71908 0,61115 0,88188 0,67862 0,89790 0,84678 0,46330 0,67591 0,50338 0,33916 0,49648 0,53330 0,52366 0,48054 0,74687 0,58398 0,77340 0,72615 0,47468 0,57482 0,49834 0,42908 0,54642 0,51868 0,56019 0,55171 0,34062 0,60430 0,36285 0,27085 0,73011 0,55340 0,75691 0,72478 0,76456 0,50137 0,78571 0,78991 0,60758 0,46409 0,63096 0,64996 0,66616 0,59398 0,69391 0,62750 0,76595 0,57299 0,74402 0,77482 0,53226 0,56143 0,52938 0,51339 0,65210 0,57569 0,68407 0,62190 0,55687 0,54630 0,58823 0,53632 0,82779 0,56820 0,84837 0,82598 0,63646 0,52353 0,63253 0,65455 0,25158 0,48530 0,26149 0,24793 0,76566 0,53693 0,78297 0,77582 0,66544 0,55563 0,69248 0,65225 0,35473 0,50851 0,36883 0,34657 0,47536 0,54117 0,50240 0,45183 0,68043 0,58309 0,71167 0,64929 0,32747 0,47152 0,34773 0,33673 0,12440 0,56551 0,13399 0,09099 0,74684 0,58395 0,77340 0,72612 0,47667 0,58016 0,50408 0,42592 0,32795 0,59106 0,35756 0,26315 0,56675 0,64000 0,45425 0,54231 Коэффициент конкордации около 65%, что в принципе совпадает с классификационной способностью модели, полученной с помощью случайного леса (100 - OOB error = 100 - 31,43 = 68,57%). Сообщение отредактировал TheThing - 3.08.2012 - 20:12 |
|
|
 |
 |
 3.08.2012 - 21:12 3.08.2012 - 21:12
Сообщение
#15
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
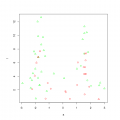
Согласно моим расчетам лишь фактор С (тяжесть состояния больного) статистически значимо ассоциирован с риском смерти (повышенный риск). Первый столбец цифр - групповые вероятности факторов А+Б+С, второй столбец - вероятности А+Б, третий столбец - А+С, четвертый - Б+С. Код plot(cmdscale(dist(rf$proximity), k=2), col=c("red","green")[factor(data.na$выжил.умер)], cex=c(seq(from=1, to=1.8, along.with=levels(factor(data.na$A))))[factor(data.na$A)]) plot(cmdscale(dist(rf$proximity), k=2), col=c("red","green")[factor(data.na$выжил.умер)], cex=c(seq(from=1, to=1.8, along.with=levels(factor(data.na$B))))[factor(data.na$B)]) plot(cmdscale(dist(rf$proximity), k=2), col=c("red","green")[factor(data.na$выжил.умер)], cex=c(seq(from=1, to=1.8, along.with=levels(factor(data.na$C))))[factor(data.na$C)]) Согласно трем графикам (по A, B, и C размер кругов) в пространстве mds полученном из proximity рандомфореста. Если и можно сомневаться в связи какого то фактора так это C Ну а разделяет группы больных B. Это очевидно из графика. Его маленькое значение во второй группе наступает ступенчато и ведет к низкому риску летального исхода. И этот фактор по мнению рандом фореста самый весомый. Два остальных фактора --- маленькие значения A в обоих группах у выздоровевших. С ведет себя аналогично A но менее выражена разница у противоположных исходов. Сообщение отредактировал p2004r - 3.08.2012 - 21:19  |
|
|
 |
 |
 3.08.2012 - 21:22 3.08.2012 - 21:22
Сообщение
#16
|
|
|
Группа: Пользователи Сообщений: 116 Регистрация: 20.02.2011 Пользователь №: 23251 |
значит логистическая регрессия и рэндом форест дают почему-то разные результаты. Нужно разбираться..
|
|
|
 |
 |
 3.08.2012 - 21:48 3.08.2012 - 21:48
Сообщение
#17
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
значит логистическая регрессия и рэндом форест дают почему-то разные результаты. Нужно разбираться.. например рандом форесту практически безразлично что B надо логарифмировать. Код > pairs(cbind(data.na[,c(2,4)], log(data.na[,3])), col=c("red","green")[factor(data.na$выжил.умер)]) > pairs(data.na[,2:4], col=c("red","green")[factor(data.na$выжил.умер)])  |
|
|
 |
 |
 3.08.2012 - 23:56 3.08.2012 - 23:56
Сообщение
#18
|
|
|
Группа: Пользователи Сообщений: 1325 Регистрация: 27.11.2007 Пользователь №: 4573 |
А если не лес строить, а одно дерево, то при одном ветвлении, на двух конечных узлах при условии С<=16,64 классификация произойдет с точностью 65,7%
Переменная С разделяет пациентов реальной выборки, а вот В не разделяет и вообще не имеет различий в группах выживших и нет ни по каким парным критериям. И не удивительно, такие разбросы данных (скорее всего ошибки ввода) например, у умерших больных есть значение 237 и 0,14. Вряд ли В может называться маркером. Но в сгенерированных выборках значения могут повторяться или вообще не попасть. ПО приведенным исходным данным точки разделения, и соответственно чувствительность и специфичность с моими расчетами не сходятся, но площадь ROC сходится, это очень странно. Автор должен верифицировать данные, иначе никакие многомерные методы на таких данных применять нельзя. Автор поста проделал часть работы и задал конкретный вопрос, как объединить результаты трех тестов. Это не задача классификации. Есть понятие положительного и отрицательного теста (найдены значения для разделения на положительный и отрицательный результат теста) и нужно узнать вероятность исхода при различных сочетаниях положительных или отрицательных тестов. Если не придираться к конкретным данным, то решить эту задачу можно следующим образом. Создать три бинарных переменных по результатам ROC, для этого использовать оптимальные точки разделения, фактор риска имеется, код 1 и нет ? 0. Эти переменные использовать в логистической регрессии. По полученным коэффициентам посчитать вероятности наступления интересующего события. При этом возможны 8 комбинаций наличия и отсутствия трех факторов риска, от отсутствия всех трех (000) до присутствия всех трех (111). Каждая из 8 групп риска будет иметь свою расчетную вероятность наступления события. При этом экспоненциальные коэффициенты уравнения регрессии для каждого предиктора будут иметь ясную интерпретацию и показывать независимый вклад каждого фактора. |
|
|
 |
 |
 4.08.2012 - 09:39 4.08.2012 - 09:39
Сообщение
#19
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
Да, я и не предполагал, что задача окажется не такой тривиальной, как мне показалось на первый взгляд. Небольшой комментарий - "С" - это оценка тяжести состояния по шкале APACHE II, которая является общепризнанной для определения риска летальности уже более 10 лет. Ошибок ввода я не нашел - "B" действительно имеет большой диапазон значений.
В любом случае, есть над чем подумать. |
|
|
 |
 |
 4.08.2012 - 10:42 4.08.2012 - 10:42
Сообщение
#20
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
А если не лес строить, а одно дерево, то при одном ветвлении, на двух конечных узлах при условии С<=16,64 классификация произойдет с точностью 65,7% Переменная С разделяет пациентов реальной выборки, а вот В не разделяет и вообще не имеет различий в группах выживших и нет ни по каким парным критериям. И не удивительно, такие разбросы данных (скорее всего ошибки ввода) например, у умерших больных есть значение 237 и 0,14. Вряд ли В может называться маркером. Но в сгенерированных выборках значения могут повторяться или вообще не попасть. ПО приведенным исходным данным точки разделения, и соответственно чувствительность и специфичность с моими расчетами не сходятся, но площадь ROC сходится, это очень странно. Автор должен верифицировать данные, иначе никакие многомерные методы на таких данных применять нельзя. 1 по мимо того что B надо логарифмировать, имеются корреляции между предикторами Код > cor(cbind(data.na[,c(2,4)], log(data.na[,3]))) A C log(data.na[, 3]) A 1.0000000 0.2813438 0.1289035 C 0.2813438 1.0000000 0.2625643 log(data.na[, 3]) 0.1289035 0.2625643 1.0000000 > cor.test(data.na[,4], data.na[,2]) Pearson's product-moment correlation data: data.na[, 4] and data.na[, 2] t = 2.4177, df = 68, p-value = 0.01831 alternative hypothesis: true correlation is not equal to 0 95 percent confidence interval: 0.04965218 0.48430137 sample estimates: cor 0.2813438 > cor.test(data.na[,4], log(data.na[,3])) Pearson's product-moment correlation data: data.na[, 4] and log(data.na[, 3]) t = 2.2439, df = 68, p-value = 0.0281 alternative hypothesis: true correlation is not equal to 0 95 percent confidence interval: 0.02940446 0.46862610 sample estimates: cor 0.2625643 > cor.test(data.na[,2], log(data.na[,3])) Pearson's product-moment correlation data: data.na[, 2] and log(data.na[, 3]) t = 1.0719, df = 68, p-value = 0.2876 alternative hypothesis: true correlation is not equal to 0 95 percent confidence interval: -0.1093837 0.3531800 sample estimates: cor 0.1289035 Группа выделена и имеет отличный состав Код > table(factor(cmdscale(dist(rf1$proximity), k=2)[,2]>0.2), factor(data.na$выжил.умер)) 0 1 FALSE 24 21 TRUE 9 16 во 2й группе исходы 9 к 16, в первой 24 к 21 вклад в разделение групп оказывает не один единственный предиктор, (B и С вместе) Кружки первая группа, треугольники вторая. (На сечении С|log(B) вообще летальные исходы сгруппировались в центре и вверху. Может отработать эту нелинейность не может при разделении групп рандомфорест. Нужен какой нибудь svm или явная трансформация данных.) Код > pairs(cbind(data.na[,c(2,4)], log(data.na[,3])), pch=c(1,2)[factor(cmdscale(dist(rf1$proximity), k=2)[,2]>0.2)], col=c("red","green")[factor(data.na$выжил.умер)]) второй вариант наоборот цветом группы, значками исходы.  |
|
|
 |
 |
 4.08.2012 - 11:18 4.08.2012 - 11:18
Сообщение
#21
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
собственно да, svm получше выделяет
Код > model <- svm( выжил.умер ~ A+B+C, data = data.na, type= "C-classification") > table(model$decision.values<=0,data.na$выжил.умер) 0 1 FALSE 25 12 TRUE 8 25 > table(model$decision.values<=-0.1,data.na$выжил.умер) 0 1 FALSE 27 13 TRUE 6 24 ## логарифмирование имеет значение!! > model <- svm( выжил.умер ~ A+log(B)+C, data = data.na, type= "C-classification") > table(model$decision.values<=-0.1,data.na$выжил.умер) 0 1 FALSE 27 9 TRUE 6 28 вот собственно он их сумел обвести Код > pairs(cbind(data.na[,c(2,4)], log(data.na[,3])), pch=c(1,2)[factor(model$decision.values<=-0.1)], col=c("red","green")[factor(data.na$выжил.умер)]) более сложное ядро в svm смогло бы осилить две области выделения. а так наверное надо просто отрезать всех явно тяжелых сначала, и потом запускать svm который научен центр резать. PS пробабилити Код > cbind(model$decision.values,data.na$выжил.умер)
0/1 1 0.98331246 0 2 0.61530576 1 3 1.00012653 0 4 -0.21684733 0 5 0.99955666 0 6 0.16078293 1 7 -1.00012726 1 8 1.14854667 1 9 -0.99985686 1 10 0.99966273 0 11 0.37811021 0 12 -0.42755238 1 13 1.00021827 0 14 1.00007588 0 15 0.76925049 0 16 0.88688175 0 17 1.01823453 0 18 0.86095764 0 19 1.01908459 0 20 1.18428922 1 21 0.45588013 1 22 -0.73663584 1 23 0.89897670 0 24 1.00026140 0 25 1.00020960 0 26 1.12620025 0 27 -0.71744634 1 28 -0.93837583 1 29 -0.99987350 1 31 -1.20454616 0 33 0.62211341 0 34 -1.37866569 1 35 -1.07486185 1 36 -1.09031422 1 37 -1.06053528 1 38 -0.50515338 1 39 -0.75995557 1 40 0.16392607 0 41 -1.00022084 1 42 0.34876086 0 43 -0.64127520 1 44 -1.15716373 1 45 0.11486255 0 46 -0.13282404 0 47 -1.04569130 0 48 0.37514348 0 49 0.56057748 0 50 0.49439228 1 51 -1.11937289 1 52 -0.89372931 1 53 -0.49529302 0 54 -0.65597539 1 55 -0.92934884 1 56 0.62306627 0 57 -1.15534228 1 58 -1.02889926 1 59 -1.00000111 1 60 0.11401070 0 61 0.68242740 1 62 -1.00003176 1 63 -0.65191720 1 64 0.74228345 1 65 -0.04860989 1 66 -1.13318704 1 67 -0.73920762 1 68 0.73537165 0 69 -1.04658105 0 70 0.16253365 0 71 -0.44523330 1 72 0.41346047 0 Сообщение отредактировал p2004r - 4.08.2012 - 11:29  |
|
|
 |
 |
 4.08.2012 - 11:41 4.08.2012 - 11:41
Сообщение
#22
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
линеаризирующее преобразование (!после отрезания всех явно тяжелых!):
1) берем точку среднее log(B) -- среднее C (или лучше среднее по шкалам mds) для летальных исходов 2) строим вектора с началом в этой точке и концом в точках наблюдений 3) новое пространство --- угол вектора vs его длинна в таком пространстве должны работать линейные методы Код > data.leit<- data.na[data.na$C<25,] > nrow(data.leit) [1] 62 > model1 <- svm( выжил.умер ~ A+log(B)+C, data = data.leit, type= "C-classification") > table(model1$decision.values<=0,data.leit$выжил.умер) 0 1 FALSE 19 5 TRUE 6 32 вот по группе без явно безнадежных (критерий C>25) svm вырезает выживших до 32. вот так решение графически выглядит Код > plot(cmdscale(dist(cbind(data.leit[,c(2,4)], log(data.leit[,3]))), k=2), col=c("red","green")[factor(data.leit$выжил.умер)], pch=c(1,2)[factor(model1$decision.values<=0)]) Трансформация Код > tapply(data.leit[,3], data.leit$выжил.умер, mean) 0 1 12.67121 20.19569 > tapply(data.leit[,4], data.leit$выжил.умер, mean) 0 1 13.48000 11.40541 > tapply(log(data.leit[,3]), data.leit$выжил.умер, mean) 0 1 1.775605 1.189165 > ((data.leit$C-12.67121)^2+(log(data.leit$B)-1.775605)^2)^0.5 [1] 5.3311377 5.1087745 2.1709325 6.0049577 6.3416986 2.5971127 [7] 7.6488885 9.4283268 2.9613371 7.3290071 2.0874944 2.6590571 [13] 0.7077666 1.7968509 1.6400452 4.3481172 1.3288040 5.5428207 [19] 2.6856595 9.7595860 3.7072333 4.6724333 4.3954970 7.6958694 [25] 7.8144577 5.1120372 3.4003874 6.7942236 0.7232215 2.2810260 [31] 0.6200533 3.0480755 5.3432953 1.8203928 12.6712147 7.3712229 [37] 2.4614863 6.8202322 4.3332743 0.6811193 10.3318129 7.2930514 [43] 9.8974529 4.0868944 2.6899526 6.9645308 2.7174036 3.7413277 [49] 2.2007804 12.0539703 3.0041289 11.3308822 8.6715569 3.7608580 [55] 7.3350855 3.3930430 4.4240841 7.5608856 6.8246717 4.3312637 [61] 10.4496927 6.0334436 > l<-((data.leit$C-12.67121)^2+(log(data.leit$B)-1.775605)^2)^0.5 > atan2(data.leit$C-12.67121, log(data.leit$B)-1.775605) [1] 1.60047511 1.01092706 -0.87854661 -1.90576287 1.63461177 2.02937132 [7] -2.08195084 1.42536019 -2.91294791 1.57849395 -2.21332718 2.61831456 [13] -1.24799125 0.18401803 0.20184394 1.66511774 1.56620199 1.29199482 [19] -1.67457571 -1.43611893 0.08880546 -1.54791341 -0.65318030 -1.65087067 [25] -1.37902877 -1.98913076 -2.23799124 -1.76137710 -1.95235967 -2.31937471 [31] 2.58268440 2.69050581 1.49709553 -1.16313148 -1.57165444 1.67814707 [37] 1.90064623 -1.78022440 1.52529843 0.50375801 1.54660568 -1.98674087 [43] -1.78502201 -2.02573395 -1.68891279 -1.27953913 1.02940171 -2.34643526 [49] 2.99163425 -1.82347545 -1.09554895 1.55157912 -1.56185158 -1.78957673 [55] 1.52936211 1.76571555 -2.16280092 1.81921224 -1.78326322 1.60459531 [61] 1.72306160 1.08266063 > a<-atan2(data.leit$C-12.67121, log(data.leit$B)-1.775605) > plot(a, l, col=c("red","green")[factor(data.leit$выжил.умер)], pch=c(1,2)[factor(model1$decision.values<=0)]) и в пространстве трансформированных шкал mds Код > data.mds<-cmdscale(dist(cbind(data.leit[,c(2,4)],log(data.leit[,3])))) > tapply(data.mds[,1], data.leit$выжил.умер, mean) 0 1 -1.2605935 0.8517523 > tapply(data.mds[,2], data.leit$выжил.умер, mean) 0 1 -0.2579902 0.1743177 > l.mds<-((data.mds[,1]+1.2605935)^2+(data.mds[,2]+0.2579902)^2)^0.5 > a.mds<-atan2(data.leit$C-12.67121, log(data.leit$B)-1.775605) > plot(a.mds, l.mds, col=c("red","green")[factor(data.leit$выжил.умер)], pch=c(1,2)[factor(model1$decision.values<=0)]) похожую трансформацию, судя по внешнему сходству, рандом_форест и пытался сделать. PS забыл отнормировать данные прежде чем считать длину вектора и угол Код > data.mds.scale<-scale(data.mds, center=c(-1.2605935, -0.2579902)) > l.mds.scale<-((data.mds.scale[,1])^2+(data.mds.scale[,2])^2)^0.5 > a.mds.scale<-atan2(data.mds.scale[,1], data.mds.scale[,2]) > plot(a.mds.scale,l.mds.scale, col=c("red","green")[factor(data.leit$выжил.умер)], , pch=c(1,2)[factor(model1$decision.values<=0)]) на картинке я зону svm приблизительно обвел, горизонтальная ось замкнута (это радианы угла вектора) поскольку все читать утомительно я резюмирую: решатель состоящий из правила -- все кто тяжелее 25 считать безнадежными и svm-решателя для остальных случаев дает 11 ошибок на 70 ~ 0.16 Сообщение отредактировал p2004r - 5.08.2012 - 12:47  |
|
|
 |
 |
 5.08.2012 - 11:23 5.08.2012 - 11:23
Сообщение
#23
|
|
|
Группа: Пользователи Сообщений: 10 Регистрация: 2.08.2012 Пользователь №: 24035 |
Коллеги, а если вернуться к посту #14, то как определить оптимальные точки разделения (cut-off) каждого из маркеров в комбинации?
|
|
|
 |
 |
 5.08.2012 - 12:55 5.08.2012 - 12:55
Сообщение
#24
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Коллеги, а если вернуться к посту #14, то как определить оптимальные точки разделения (cut-off) каждого из маркеров в комбинации? точка оптимальная считается для некого индекса по комбинации маркеров, рассчитанная отдельно по маркеру эта точка в функцию развернется. (фактически зона svm решения это и есть "по маркерам" построенная "точка разделения") то есть --- сначала считать индекс, потом для индекса точку отсечения. если это имелось в виду то в ROC пакет обычно входит соответствующая функция. например в pROC это coords Код If ?x="best"?, the ?best.method? argument controls how the optimal
threshold is determined. ?youden? Youden's J statistic (Youden, 1950) is employed. The optimal cut-off is the threshold that maximizes the distance to the identity (diagonal) line. Can be shortened to ?y?. The optimality criterion is: max(sensitivities + specificities) ?closest.topleft? The optimal threshold is the point closest to the top-left part of the plot with perfect sensitivity or specificity. Can be shortened to ?c? or ?t?. The optimality criterion is: min((1 - sensitivities)^2 + (1- specificities)^2) In addition, weights can be supplied if false positive and false negative predictions are not equivalent: a numeric vector of length 2 to the ?best.weights? argument. The indices define 1. the cost of of a false negative classification 2. the prevalence, or the proportion of cases in the total population (n.cases/(n.controls+n.cases)). : The optimality criteria are modified as proposed by Perkins and Schisterman: ?youden? max(sensitivities + r \times specificities) ?closest.topleft? min((1 - sensitivities)^2 + r \times (1- specificities)^2) with r = (1 - prevalence) / (cost * prevalence) By default, prevalence is 0.5 and cost is 1 so that no weight is applied in effect. Note that several thresholds might be equally optimal.  |
|
|
 |
 |
 5.08.2012 - 15:37 5.08.2012 - 15:37
Сообщение
#25
|
||
|
Группа: Пользователи Сообщений: 116 Регистрация: 20.02.2011 Пользователь №: 23251 |
Решил сделать рэндом форест, а также построить простое CART, чтобы понять почему результаты расходятся с логистической регрессией и с результатами p2004r. Как выяснилось, все со всем сходится
Сначала рендом форест с 3 исходными предикторами: randomForest(formula = Group ~ ., data = crs$dataset[, c(crs$input, crs$target)], ntree = 500, mtry = 1, importance = TRUE, replace = FALSE, na.action = na.roughfix) Type of random forest: classification Number of trees: 500 No. of variables tried at each split: 1 OOB estimate of error rate: 27.78% Confusion matrix: alive dead class.error alive 30 9 0.2307692 dead 11 22 0.3333333 Analysis of the Area Under the Curve (AUC) ========================================== Call: roc.default(response = crs$rf$y, predictor = crs$rf$votes) Data: crs$rf$votes in 39 controls (crs$rf$y alive) > 33 cases (crs$rf$y dead). Area under the curve: 0.7584 95% CI: 0.6462-0.8706 (DeLong) Variable Importance =================== alive dead MeanDecreaseAccuracy C 2.87 3.59 2.67 B 1.90 3.03 2.14 A 1.89 1.65 1.59 Ошибка OOB составляет 27,78%, что в принципе говорит, что модель неплохая (AUC = 75%)/ На первом месте по важности предикторов выступает фактор С, затем В и лишь в конце болтается А. Решил убрать фактор А из модели и посмотреть насколько изменится классификационная способность. Вот что получилось: OOB estimate of error rate: 31.94% Confusion matrix: alive dead class.error alive 28 11 0.2820513 dead 12 21 0.3636364 Analysis of the Area Under the Curve (AUC) ========================================== Call: roc.default(response = crs$rf$y, predictor = crs$rf$votes) Data: crs$rf$votes in 39 controls (crs$rf$y alive) > 33 cases (crs$rf$y dead). Area under the curve: 0.7599 95% CI: 0.6499-0.8699 (DeLong) Variable Importance =================== alive dead MeanDecreaseAccuracy C 3.51 4.77 3.26 B 1.69 3.40 2.24 Видим, что OOB увеличилась на пару процентов, а AUC остался прежним, фактор С опять на 1 месте по важности. Поэтому я бы предиктор А вообще-бы не включал в модель, а рассматривал его как ненужный "шум". Затем построил простое CART и получил результат, который полностью совпал с методом опорных векторов (svm) в подсчетах p2004r, логистической регрессией и random forest. Хорошо то, что хорошо заканчивается |
|
|
|
 |
 |
 5.08.2012 - 15:56 5.08.2012 - 15:56
Сообщение
#26
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
и все таки, после применения правила С>25, остается смесь из 62 случаев, которую svm пилит с вероятностью ошибки (5+6)/(19+5+6+32) ~ 0.1774194
у выживших разброс в двумерном распределении C - log(B) больше чем у летальных исходов. Сообщение отредактировал p2004r - 5.08.2012 - 15:57  |
|
|
 |
 |
 5.08.2012 - 16:40 5.08.2012 - 16:40
Сообщение
#27
|
|
|
Группа: Пользователи Сообщений: 116 Регистрация: 20.02.2011 Пользователь №: 23251 |
Кстати, вот хорошая статья, где проводился сравнительный анализ support vector machines, logistic regression, random forest, CART, neural netss, boosted trees, bagged trees, naive Bayes и др. Согласно результатам, на первом месте - бустид-деревья, второе - рэндом форест, третье - опорные вектора.
 empirical.icml06.pdf ( 124,37 килобайт )
Кол-во скачиваний: 404
empirical.icml06.pdf ( 124,37 килобайт )
Кол-во скачиваний: 404Сообщение отредактировал TheThing - 5.08.2012 - 16:41 |
|
|
 |
 |
 5.08.2012 - 19:05 5.08.2012 - 19:05
Сообщение
#28
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Согласно результатам, на первом месте - бустид-деревья, второе - рэндом форест, третье - опорные вектора. Спасибо! для интерполяции (ну и вырезания "хитрых областей", например "вложенная спираль" или вообще структурные данные типа языковых конструкций) svm хорош, правда надо вид ядра подбирать и за регуляризацией следить что бы экстраполяция не страдала.  |
|
|
 |
 |
 16.08.2012 - 09:25 16.08.2012 - 09:25
Сообщение
#29
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
Раз зашла речь про ROC-анализ в программе SPSS подскажите как определить Точки разделения для факторов риска чтоб выявить риск развития осложнений в зависимости от них. прилагаю результаты логистической регрессии. Есть ли программа SPSS в бесплатном доступе или лучше воспользоваться MEDCALC. у мнея еще вопрос. для фактора риска ИБС очень широкий ДИ, как мне это интерпретировать
Прикрепленные файлы
|
|
|
 |
 |
 16.08.2012 - 15:38 16.08.2012 - 15:38
Сообщение
#30
|
|
|
Группа: Пользователи Сообщений: 116 Регистрация: 20.02.2011 Пользователь №: 23251 |
Раз зашла речь про ROC-анализ в программе SPSS подскажите как определить Точки разделения для факторов риска чтоб выявить риск развития осложнений в зависимости от них. прилагаю результаты логистической регрессии. Есть ли программа SPSS в бесплатном доступе или лучше воспользоваться MEDCALC. у мнея еще вопрос. для фактора риска ИБС очень широкий ДИ, как мне это интерпретировать В бесплатном доступе SPSS нет, есть в пиратском. Логистическая регрессия как линейный параметрический классификатор очень плохо справляется с задачами, где наблюдается большое количество предикторов (больше 10, у Вас их больше 20), поскольку наблюдается "curse of dimentionality" - проклятие размерности, особенно при таких небольших выборках (относительно к количеству независимых переменных). Все это выливается в biased (искаженные) коэффициенты регрессии, большие стандартный ошибки и огромные ДИ. Расчет необходимой выборки для логит-регрессии - задача оч. непростая. Peduzzi et al. (1996) предложили упрощенный вариант: N = 10 k / p k - количество предикторов р - наименьшая пропорция негативных/позитивных случаев У Вас к равняется 23, допустим р равняется 0.3 (то есть 30% людей в выборке больных, а 70% здоровых), следовательно: N = 10 * 23 / 0,3 = 766 человек. Это минимальное количество людей, если Вы хотите анализировать 23 предиктора. Если это значение получилось бы меньше 100, его следует увеличить до 100, как советует Long (1997). Выходов несколько: 1) увеличивать выборку 2) уменьшать количество предикторов 3) применять соответствующие методы (а лучше их совокупность), которые лишены проблем логит-регрессии. P.S. p-value в логит-регрессии - это не стат. значимость отношения шансов. |
|
|
 |
 |
 16.08.2012 - 20:10 16.08.2012 - 20:10
Сообщение
#31
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
В бесплатном доступе SPSS нет, есть в пиратском. Логистическая регрессия как линейный параметрический классификатор очень плохо справляется с задачами, где наблюдается большое количество предикторов (больше 10, у Вас их больше 20), поскольку наблюдается "curse of dimentionality" - проклятие размерности, особенно при таких небольших выборках (относительно к количеству независимых переменных). Все это выливается в biased (искаженные) коэффициенты регрессии, большие стандартный ошибки и огромные ДИ. Расчет необходимой выборки для логит-регрессии - задача оч. непростая. Peduzzi et al. (1996) предложили упрощенный вариант: N = 10 k / p k - количество предикторов р - наименьшая пропорция негативных/позитивных случаев У Вас к равняется 23, допустим р равняется 0.3 (то есть 30% людей в выборке больных, а 70% здоровых), следовательно: N = 10 * 23 / 0,3 = 766 человек. Это минимальное количество людей, если Вы хотите анализировать 23 предиктора. Если это значение получилось бы меньше 100, его следует увеличить до 100, как советует Long (1997). Выходов несколько: 1) увеличивать выборку 2) уменьшать количество предикторов 3) применять соответствующие методы (а лучше их совокупность), которые лишены проблем логит-регрессии. P.S. p-value в логит-регрессии - это не стат. значимость отношения шансов. Спасибо, уже для меня начало что то проясняться. но, к сожалению, не смогу увеличить объем выборки, тогда мне остается уменьшить количество предикторов, только не знаю как- либо отсеять логически или может нужно их как то проанализировать стат.методом. Расскажите , пожалуйста, подробней про 3 вывод |
|
|
 |
 |
 16.08.2012 - 21:53 16.08.2012 - 21:53
Сообщение
#32
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Спасибо, уже для меня начало что то проясняться. но, к сожалению, не смогу увеличить объем выборки, тогда мне остается уменьшить количество предикторов, только не знаю как- либо отсеять логически или может нужно их как то проанализировать стат.методом. Расскажите , пожалуйста, подробней про 3 вывод так а где сами данные?  |
|
|
 |
 |
 16.08.2012 - 22:34 16.08.2012 - 22:34
Сообщение
#33
|
|
|
Группа: Пользователи Сообщений: 116 Регистрация: 20.02.2011 Пользователь №: 23251 |
Спасибо, уже для меня начало что то проясняться. но, к сожалению, не смогу увеличить объем выборки, тогда мне остается уменьшить количество предикторов, только не знаю как- либо отсеять логически или может нужно их как то проанализировать стат.методом. Расскажите , пожалуйста, подробней про 3 вывод Выводов у меня не было, были возможные выХоды из ситуации Данные действительно бы пригодились.. |
|
|
 |
 |
 17.08.2012 - 09:02 17.08.2012 - 09:02
Сообщение
#34
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
КФР-контролируемый фактор риска, НФР-неконтролируемый ФР, ЗАДАЧА- выявить наиболее вероятные факторы риска для прогнозирования развития кардиальных осложнений в послеоперационном периоде
Сообщение отредактировал Диана - 31.08.2012 - 09:46 |
|
|
 |
 |
 17.08.2012 - 15:28 17.08.2012 - 15:28
Сообщение
#35
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
КФР-контролируемый фактор риска, НФР-неконтролируемый ФР, ЗАДАЧА- выявить наиболее вероятные факторы риска для прогнозирования развития кардиальных осложнений в послеоперационном периоде много пропущенных данных... будет интересно у меня после импорта данных (там иногда попадаются точки в ячейках, нельзя ли сохранить таблицу с простым заголовком в старом эксель формате? а то я не уверен в корректности импорта) получились вот такие переменные: Код > names(read.csv2("mp3gl.csv")) [1] "ФИО.шифр" "пол" [3] "возраст" "ИМТ..кг.м2" [5] "ИМТ" "S.тела.по.Дюб" [7] "к.во.дней.до.опер" "к.во.дней.после.опер" [9] "время.уст..я.д.за.анев" "кардио.жалобы" [11] "длит.кардиожалоб" "хирург.жалобы" [13] "группы.по.лечению" "п.о.кард.осложн" [15] "Кард.осл.я" "летальность" [17] "стресс.ЭхоКГ" "к.во.зон.гипо.и.акинезии" [19] "X" "X.1" [21] "ГБ" "X.2" [23] "ГБ.ГЛЖ" "ИБС..стенокардия" [25] "постинф.кардиоскл" "НК..фк" [27] "ДЛП" "размер.АБА" [29] "синдромность" "прех.ишем.послеопер" [31] "СД" "доступ" [33] "курение" "диаст..Дисфункция00" [35] "САД1" "ДАД1" [37] "ЧСС1" "САД5" [39] "ДАД5" "ЧСС5" [41] "САД.д.о" "ДАД.д.о" [43] "ЧСС.д.о" "САД.п.о" [45] "ДАД.п.о" "ЧСС.п.о" [47] "бета.блокеры" "ББдоза" [49] "ББкол.во.суток.назн" "антаг.кальция" [51] "АКдоза.суточная" "АКкол.во.сут.назн" [53] "антиагреганты" "инг.АПФ" [55] "ИАПФсут.доза" "ИАПФкол.во.сут.назн" [57] "нитраты" "дигоксин" [59] "диуретики" "кордарон" [61] "гепарин" "трад.тер" [63] "операция1" "доступ1" [65] "время.операции1" "Время.опер.11" [67] "Время.опер.21" "Время.опер.31" [69] "время.переж.аорты1" "Вр.переж.аорты11" [71] "Вр.переж.аорты21" "кровопотеря1" [73] "кровопотеря11" "наруш.ритма00" [75] "рубц.измен00" "ЧСС00" [77] "ритм00" "наруш.пров00" [79] "PQ" "QRS" [81] "QT" "ST" [83] "з.Т" "Соколов.Лайон" [85] "корн..Индекс" "корн..Произв.е" [87] "минЧСС" "максЧСС" [89] "средЧСС" "ЖЭС" [91] "ЖЭС..к.во" "ЖТ" [93] "НЖЭС..к.во" "НЖТ..к.во" [95] "депрессия.ST" "АВ.блокады" [97] "пароксизмы.ФП" "ГЛЖ00" [99] "X.3" "зоны.гипо.и.акин00" [101] "КДР..см00" "КСР..см00" [103] "КДО..мл00" "индекс.КДО..00" [105] "КСО00" "инд.КСО00" [107] "ФВ00" "УО00" [109] "ТМЖП00" "ТЗСТ.ЛЖ00" [111] "X.4" "ММ.ЛЖ.формула.Devereux" [113] "ИММ.ЛЖ" "ПЗРВТ.00" [115] "КДР.ПЖ00" "ЛП00" [117] "d.аорты00" "ГДС.СДЛА00" [119] "диаст..Дисфункция00.1" "кальциноз.аорты00" [121] "наруш.ритма11" "ЧСС11" [123] "PQ11" "QRS11" [125] "QT11" "депрессия.ST11" [127] "з.Т11" "длит.ть.прех.ишемии11" [129] "очаг.измен11" "мин.ЧСС11" [131] "макс.ЧСС11" "средняя.ЧСС11" [133] "ЖЭС.по.Лауну11" "ЖЭС..к.во11" [135] "парные.ЖЭС11" "ЖТ11" [137] "НЖЭС.к.во11" "НЖТ.к.во11" [139] "депрессия.SТ11" "нар.е.пров11" [141] "пароксизмы.ФП11" "п.о.гипокинезия11" [143] "КДР11" "КСР11" [145] "КДО11" "инд.КДО11" [147] "КСО11" "инд.КСО11" [149] "ФВ11" "УО11" [151] "ТМЖП11" "ТЗСТ.ЛЖ11" [153] "ММ.ЛЖ.формула.Devereux.1" "ИММ.ЛЖ.1" [155] "ПЗРВТ.11" "КДР.ПЖ11" [157] "ЛП11" "d.аорты11" [159] "ГДС.СДЛА11" "бета.блокеры11" [161] "доза11ББ" "ББкол.во.суток.назначения.пре11" [163] "антагонисты.кальция11" "АГдоза.суточная11" [165] "АГкол.во.суток.назн11" "антиагреганты11" [167] "инг.АПФ11" "ИАПФсуточная.доза11" [169] "ИАПФкол.во.суток.назн11" "нитраты11" [171] "дигоксин11" "диуретики11" [173] "кордарон11" "гепарин11" [175] "трад.терапия11" какие номера являются осложнениями? или какие являются предикторами? вот например я предполагаю что осложнение это: Код > (read.csv2("mp3gl.csv")$"постинф.кардиоскл") [1] 1 1 1 1 0 1 1 1 0 0 0 1 1 0 1 0 1 0 0 1 1 0 1 0 0 1 0 0 0 1 0 0 0 0 0 0 0 0 [39] 1 0 1 1 0 0 0 1 0 0 0 0 1 0 0 0 0 0 0 0 0 0 0 0 1 1 0 0 1 1 0 0 0 0 0 0 0 1 [77] 0 0 0 0 0 0 0 1 0 1 1 0 0 1 1 0 0 0 0 а предикторы это со 2 по 18ю Код > names(data[,2:18]) [1] "пол" "возраст" [3] "ИМТ..кг.м2" "ИМТ" [5] "S.тела.по.Дюб" "к.во.дней.до.опер" [7] "к.во.дней.после.опер" "время.уст..я.д.за.анев" [9] "кардио.жалобы" "длит.кардиожалоб" [11] "хирург.жалобы" "группы.по.лечению" [13] "п.о.кард.осложн" "Кард.осл.я" [15] "летальность" "стресс.ЭхоКГ" [17] "к.во.зон.гипо.и.акинезии" поскольку среди предикторов много пропусков перед нами два пути: 1) исключить случаи в которых есть пропуски Код > data.na<-na.omit(data[,c(2:18,25)]) > table(data.na$постинф.кардиоскл) 0 1 8 18 > rf<-randomForest(data.na[,-18],factor(data.na$"постинф.кардиоскл"), proximity=TRUE) > rf Call: randomForest(x = data.na[, -18], y = factor(data.na$постинф.кардиоскл), proximity = TRUE) Type of random forest: classification Number of trees: 500 No. of variables tried at each split: 4 OOB estimate of error rate: 38.46% Confusion matrix: 0 1 class.error 0 0 8 1.0000000 1 2 16 0.1111111 > MDSplot(rf, factor(data.na$"постинф.кардиоскл"), k=3) > varImpPlot(rf) как видим ничего в таком варианте модель не разделяет ничего. 2) заполним пропущенные случаи прибегнув к множественной импутации Код > data.2.18.impute<-rfImpute(data[,2:18],factor(data$"постинф.кардиоскл"), iter=5) ntree OOB 1 2 300: 26.32% 10.94% 58.06% ntree OOB 1 2 300: 27.37% 14.06% 54.84% ntree OOB 1 2 300: 27.37% 15.62% 51.61% ntree OOB 1 2 300: 26.32% 14.06% 51.61% ntree OOB 1 2 300: 29.47% 17.19% 54.84% > rf.impute<-randomForest(data.2.18.impute[,-1],data.2.18.impute[,1], proximity=TRUE) > rf.impute Call: randomForest(x = data.2.18.impute[, -1], y = data.2.18.impute[, 1], proximity = TRUE) Type of random forest: classification Number of trees: 500 No. of variables tried at each split: 4 OOB estimate of error rate: 29.47% Confusion matrix: 0 1 class.error 0 54 10 0.1562500 1 18 13 0.5806452 > MDSplot(rf.impute, data.2.18.impute[,1], k=3) > varImpPlot(rf.impute) > plot(importance(rf.impute),varUsed(rf.impute)) > text(importance(rf.impute),varUsed(rf.impute), labels= names(data.2.18.impute[,-1])) получается имеют влияние предикторы: "ИМТ..кг.м2", "к.во.зон.гипо.и.акинезии", "длит.кардиожалоб", "возраст", "к.во.дней.после.опер". меньше влияет "к.во.дней.до.опер". и совсем слабо (но еще влияет) "S.тела.по.Дюб", "кардио.жалобы", "стресс.ЭхоКГ", "хирург.жалобы", "группы.по.лечению". Естественно эту информацию можно накопить относительно различных осложнений и построить общую картину. Так какие показатели являются осложнениями? или какие являются предикторами к осложнениям? Скорее всего "группы.по.лечению" я зря в предикторы включал?  |
|
|
 |
 |
 17.08.2012 - 18:05 17.08.2012 - 18:05
Сообщение
#36
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
я немножко сократила таблицу, убрала малоинтересующие данные. желтым цветом выделила неконтролируемые факторы риска, синим- контролируемые. красный цвет- осложнений. цель- узнать как влияет кардиопротекторная терапия- то есть группы лечения-серый цвет.[ в группе 1 и 2 под влиянием терапии происходит урежение ЧсС(ЧСС д/о) и меньше случаев тахикардии (чсс больше 100) в послеоперационном периоде( считается, что тахикардия индуцирует ишемию миокарда и, в свою очередь, инфаркт миокарда)] на развитие кардиальных осложнений
Сообщение отредактировал Диана - 31.08.2012 - 09:47 |
|
|
 |
 |
 17.08.2012 - 22:26 17.08.2012 - 22:26
Сообщение
#37
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
я немножко сократила таблицу, убрала малоинтересующие данные. желтым цветом выделила неконтролируемые факторы риска, синим- контролируемые. красный цвет- осложнений. цель- узнать как влияет кардиопротекторная терапия- то есть группы лечения-серый цвет.[ в группе 1 и 2 под влиянием терапии происходит урежение ЧсС(ЧСС д/о) и меньше случаев тахикардии (чсс больше 100) в послеоперационном периоде( считается, что тахикардия индуцирует ишемию миокарда и, в свою очередь, инфаркт миокарда)] на развитие кардиальных осложнений я попробую сказать конкретнее я вижу Ваш эксель файл (кстати Вы так и не соблаговолили его сохранить в старом формате екселя) как показано на присоединенном скриншоте. в файле сохраняются какие то точки в отдельных полях. давайте обсуждать список переменных датасета который я уже один раз почистил. мне нужно знать какие номера переменных являются предикторами, а какие "факторами риска". это всего два списка  |
|
|
 |
 |
 18.08.2012 - 08:58 18.08.2012 - 08:58
Сообщение
#38
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
Факторы риска:
2 3 5 17 20 22 - 34 64 68 70 73 колонки 44-46 закодировала 0/1(44А, 45А,46А) предикторы 44А 45А 46А 118 извините, что не сохранила файл в старом формате Заранее спасибо Сообщение отредактировал Диана - 9.09.2012 - 22:26 |
|
|
 |
 |
 18.08.2012 - 13:18 18.08.2012 - 13:18
Сообщение
#39
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Факторы риска: 2 3 5 17 20 22 - 34 64 68 70 73 колонки 44-46 закодировала 0/1(44А, 45А,46А) предикторы 44А 45А 46А 118 извините, что не сохранила файл в старом формате Заранее спасибо вот это --- "колонки 44-46 закодировала 0/1(44А, 45А,46А)" было сделано зря. В таком виде никакого разделения практически нет. надо вернуть прежнюю шкалу и тогда (как мне кажется) удастся построить с помощью случайного леса регрессию. 118 дал разделение Код > data2.varset1.impute.X118<-rfImpute(data2.varset1,factor(data2$X118), iter=5) ntree OOB 1 2 300: 16.84% 10.91% 25.00% ntree OOB 1 2 300: 22.11% 14.55% 32.50% ntree OOB 1 2 300: 21.05% 12.73% 32.50% ntree OOB 1 2 300: 20.00% 12.73% 30.00% ntree OOB 1 2 300: 20.00% 12.73% 30.00% > rf.data2.varset1.impute.X118.best<-tuneRF(data2.varset1.impute.X118[,-1],factor(data2$X118), proximity=TRUE, doBest=TRUE) mtry = 4 OOB error = 24.21% Searching left ... mtry = 2 OOB error = 23.16% 0.04347826 0.05 Searching right ... mtry = 8 OOB error = 22.11% 0.08695652 0.05 mtry = 16 OOB error = 20% 0.0952381 0.05 mtry = 22 OOB error = 23.16% -0.1578947 0.05 > rf.data2.varset1.impute.X118.best Call: randomForest(x = x, y = y, mtry = res[which.min(res[, 2]), 1], proximity = TRUE) Type of random forest: classification Number of trees: 500 No. of variables tried at each split: 16 OOB estimate of error rate: 20% Confusion matrix: 0 1 class.error 0 46 9 0.1636364 1 10 30 0.2500000 > MDSplot(rf.data2.varset1.impute.X118.best, factor(data2$X118), k=3) > varImpPlot(rf.data2.varset1.impute.X118.best) > plot(importance(rf.data2.varset1.impute.X118.best),varUsed(rf.data2.varset1.impute.X118.best)) > text(importance(rf.data2.varset1.impute.X118.best),varUsed(rf.data2.varset1.impute.X118.best), labels= names(data2.varset1.impute.X118[,-1]), pos=4) имеет значение только [30,] "X30" "прех.ишем.послеопер" [3,] "X3" "возраст" что вполне подтверждается графиком > mosaicplot(table(data2$X30, cut(data2$X3, hist(data2$X3, plot=FALSE)$breaks), data2$X118)) Оценим пригодность модели для диагностики с помощью ROC. Код > plot(roc(data2$X118, rf.data2.varset1.impute.X118.best$votes[,2]), print.auc=TRUE) Call: roc.default(response = data2$X118, predictor = rf.data2.varset1.impute.X118.best$votes[, 2]) Data: rf.data2.varset1.impute.X118.best$votes[, 2] in 55 controls (data2$X118 0) < 40 cases (data2$X118 1). Area under the curve: 0.8111 Судя по области решения, которую надо вырезать в пространстве сформированном mds по восстановленным случайным лесом расстояниям между экспериментальными случаями, лучше с разделением справится svm. Случайный лес похоже не дотягивается до случаев со средним возрастом из основной группы. Сообщение отредактировал p2004r - 18.08.2012 - 13:35  |
|
|
 |
 |
 18.08.2012 - 20:57 18.08.2012 - 20:57
Сообщение
#40
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
спасибо за помощь. колонки 44-46 не имеют влияние? посоветуйте мне, пожалуйста, литературу, чтоб я поняла все это, поскольку я все еще плохо дружу со статистикой. по моим расчетам вид лечения(группы по лечению) до операции не влияет на осложнения, а мне желательно доказать обратное. я сокращала все осложнения до фатальные и нефатальные-тоже нет желаемого результата, только отмечено снижение летальности в 1 группе по сравнению с 3й.
|
|
|
 |
 |
 18.08.2012 - 22:37 18.08.2012 - 22:37
Сообщение
#41
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
спасибо за помощь. колонки 44-46 не имеют влияние? посоветуйте мне, пожалуйста, литературу, чтоб я поняла все это, поскольку я все еще плохо дружу со статистикой. по моим расчетам вид лечения(группы по лечению) до операции не влияет на осложнения, а мне желательно доказать обратное. я сокращала все осложнения до фатальные и нефатальные-тоже нет желаемого результата, только отмечено снижение летальности в 1 группе по сравнению с 3й. 0. Прочитать любую книгу про методы многомерного анализа данных. 1. Анализ показывает только то, что колонки 44А, 45А, 46А (в виде 0-1) невозможно разделить с помощью 2 3 5 17 20 22 - 34 64 68 70 73. Колонки 44, 45, 46 в набор тех с помощью которых пытаемся разделять я не включал, поскольку это не следовало из Вашего описания. Увы, но за Вас я не могу придумать какой набор переменных какую переменную должен попытаться оценить. 2. (еще раз) То что 44А, 45А, 46А перекодировали в 0-1 плохо, это потеря информации. Случайным лесом можно строить не только модель классифицирующую, но и регрессионную. возможно что тогда зависимость станет очевидной. 3. Группы лечения это переменная 13? или какая?  |
|
|
 |
 |
 19.08.2012 - 09:21 19.08.2012 - 09:21
Сообщение
#42
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
|
|
|
 |
 |
 26.08.2012 - 08:57 26.08.2012 - 08:57
Сообщение
#43
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
Подскажите кто знает: возможно ли удалить выложенные данные
|
|
|
 |
 |
 26.08.2012 - 08:59 26.08.2012 - 08:59
Сообщение
#44
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
ничего не получается, от проводимого лечения нет достоверного влияния на снижение осложнений
|
|
|
 |
 |
 27.08.2012 - 15:12 27.08.2012 - 15:12
Сообщение
#45
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
ничего не получается, от проводимого лечения нет достоверного влияния на снижение осложнений Немного был занят. 1) "группы.по.лечению" это что за переменная? это она описывает проводимое лечение? 2) в конце первого файла данных были всякие "дигоксины", они имеют отношение к проводимому лечению?  |
|
|
 |
 |
 27.08.2012 - 16:58 27.08.2012 - 16:58
Сообщение
#46
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
Немного был занят. 1) "группы.по.лечению" это что за переменная? это она описывает проводимое лечение? 2) в конце первого файла данных были всякие "дигоксины", они имеют отношение к проводимому лечению? здравствуйте. лечение - колонки 47-62, а колонка 13 группы по лечению- делит всех пациентов на 3 группы задачи исследования: 1. влияет ли снижение ЧСС до операции на снижение частоты кардиальных осложнений 2. влияет ли тип операции на снижение частоты кардиальных осложнений 3. влияние факторов риска |
|
|
 |
 |
 27.08.2012 - 17:14 27.08.2012 - 17:14
Сообщение
#47
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
здравствуйте. лечение - колонки 47-62, а колонка 13 группы по лечению- делит всех пациентов на 3 группы задачи исследования: 1. влияет ли снижение ЧСС до операции на снижение частоты кардиальных осложнений 2. влияет ли тип операции на снижение частоты кардиальных осложнений 3. влияние факторов риска Не совсем понимаю Хорошо, 13 колонка делит пациентов на 3 группы. Лечение в группах было разное? Можно эту колонку использовать как признак назначенного лечения? Иными словами какой принцип разбиения пациентов на эти три группы? 1) влияет ли снижение ЧСС до операции на снижение частоты кардиальных осложнений в какой колонке находится "снижение ЧСС до операции", и в какой колонке соответственно "частота кардиальных осложнений"? 2) влияет ли тип операции на снижение частоты кардиальных осложнений колонка "тип операции" какой номер? 3) влияние факторов риска на что влияние? на какую колонку? ну и номера колонок "факторов риска" укажите.  |
|
|
 |
 |
 27.08.2012 - 17:25 27.08.2012 - 17:25
Сообщение
#48
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
Хорошо, 13 колонка делит пациентов на 3 группы. Лечение в группах было разное? Можно эту колонку использовать как признак назначенного лечения? Иными словами какой принцип разбиения пациентов на эти три группы? можно, принцип разбиения-по проводимой терапии(1-бетаблокаторы, 2 - антагонисты кальция, 3 - ингибиторы АПФ Сообщение отредактировал Диана - 27.08.2012 - 17:29 |
|
|
 |
 |
 27.08.2012 - 17:29 27.08.2012 - 17:29
Сообщение
#49
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
1) влияет ли снижение ЧСС до операции на снижение частоты кардиальных осложнений в какой колонке находится "снижение ЧСС до операции", - колонка 43, ( может надо подсчитать на сколько снизилась от первоначального при поступлении в стационар), и в какой колонке соответственно "частота кардиальных осложнений"?-колонка 14 Сообщение отредактировал Диана - 27.08.2012 - 17:29 |
|
|
 |
 |
 27.08.2012 - 17:42 27.08.2012 - 17:42
Сообщение
#50
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
2) "влияет ли тип операции на снижение частоты кардиальных осложнений колонка "тип операции" какой номер? " - колонка- 64 (два вида доступа), и обьем операции - 63,65, 69, 72 3) влияние факторов риска "на что влияние? на какую колонку?" - 14 ( п/о кард. осложнения), ну и номера колонок "факторов риска" укажите колонки- 2, 3, 4, 17, 20 - 34, 44, 45, 46. [/quote] |
|
|
 |
 |
 27.08.2012 - 22:24 27.08.2012 - 22:24
Сообщение
#51
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
1) влияет ли снижение ЧСС до операции на снижение частоты кардиальных осложнений в какой колонке находится "снижение ЧСС до операции", - колонка 43, ( может надо подсчитать на сколько снизилась от первоначального при поступлении в стационар), и в какой колонке соответственно "частота кардиальных осложнений"?-колонка 14 ну сначала давайте посмотрим глазами на то как влияет или нет. вот график (mosaicplot) показывающий частоту случаев с определенным сочетанием трех переменных --- группа лечения (13), частота осложнений (14), и сгруппированная выше и ниже собственной медианы ЧСС (43). как видно --- осложнения нарастают от первой группы к третьей, ЧСС также нарастает в данном направлении + дополнительно резко нарастает во второй и третей группе лечения при наличии осложнения любой степени Код mosaicplot(table(data[,13], data[,14], cut(data[,43], c(50,70,120)))) с ростом частоты осложнений (от группы лечения 1 к 3) незначительно увеличивается доля 2 го типа доступа (64) Код mosaicplot(table(data[,13], data[,14], data[,64])) Объем операции 63 нарастает. Код > summary(data[,63]) Min. 1st Qu. Median Mean 3rd Qu. Max. 1.000 1.000 1.000 1.453 2.000 4.000 > mosaicplot(table(data[,13], data[,14], data[,63])) Объем операции 65 падает. Код > summary(data[,65]) Min. 1st Qu. Median Mean 3rd Qu. Max. 85.0 135.0 155.0 166.2 185.0 320.0 > mosaicplot(table(data[,13], data[,14], cut(data[,65], c(80,155,330)) )) Объем 69.... наверное лучше объединить все случаи осложнений в один уровень, вот так лучше. Видно сразу что ситуация во второй группе и третьей группе типа лечения по отношению к объему 69 зеркальна Код > summary(data[,69]) Min. 1st Qu. Median Mean 3rd Qu. Max. 15.00 35.00 43.00 45.06 50.00 104.00 > mosaicplot(table(data[,13], data[,14]>0, cut(data[,69], c(10,43,110)) )) > Объем 72 постояненное соотношение у не осложненных во всех трех группах лечения, но у осложненных доля объема падает и в третей группе достигает уровня неосложненных. Скорее всего это фактор который указывает на возникновения осложнения вследствии каких то причин во время операции. Код > summary(data[,72]) Min. 1st Qu. Median Mean 3rd Qu. Max. 200.0 400.0 500.0 592.6 700.0 2500.0 > mosaicplot(table(data[,13], data[,14]>0, cut(data[,72], c(100,500,3000)) )) > PS добавил первые мозаики с объединенными осложениями Сообщение отредактировал p2004r - 27.08.2012 - 23:35  |
|
|
 |
 |
 28.08.2012 - 09:02 28.08.2012 - 09:02
Сообщение
#52
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
супер, в мозаичных графиках данные очень наглядно смотрятся, буду их использовать в своей работе
|
|
|
 |
 |
 28.08.2012 - 12:07 28.08.2012 - 12:07
Сообщение
#53
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
супер, в мозаичных графиках данные очень наглядно смотрятся, буду их использовать в своей работе ну а те зависимости, что видны на "мозаике" можно подтверждать результатами факторного дисперсионного анализа.  |
|
|
 |
 |
 28.08.2012 - 13:46 28.08.2012 - 13:46
Сообщение
#54
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
у меня есть данные факторного анализа, но, как сейчас обратила внимание, там нет некоторых переменных, которые использовали при построении мозаичных графиков
Сообщение отредактировал Диана - 1.10.2012 - 09:15 |
|
|
 |
 |
 28.08.2012 - 19:54 28.08.2012 - 19:54
Сообщение
#55
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
у меня есть данные факторного анализа, но, как сейчас обратила внимание, там нет некоторых переменных, которые использовали при построении мозаичных графиков В данном случае речь шла о факторном дисперсионном анализе. Если все переделать в номинальную шкалу, то подойдет multiple correspondence analysis. Если не переделывать, то multivariate analysis with mixed quantitative variables and factors (например dudi.mix из ade4). но это ж мне каждую переменную смотреть и решать что она такое  |
|
|
 |
 |
 28.08.2012 - 21:10 28.08.2012 - 21:10
Сообщение
#56
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
|
|
|
 |
 |
 31.08.2012 - 16:49 31.08.2012 - 16:49
Сообщение
#57
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
взял показатели без пропусков. 1) смотрим чем отличаются (и можно ли различить группы лечения) Код tmp <- as.vector(table(factor(data2[,13]))); num_clases <- length(tmp); min_size <- tmp[order(tmp,decreasing=FALSE)[1]]; vector_for_sampsize.13 <- rep(min_size,num_clases); rf<-randomForest(data.frame(data2[,c( 65, 69, 72, 43, 3)], factor(data2[,63]), factor(data2[,2]) , factor(data2[,14]>0)), factor(data2[,13]), sampsize=vector_for_sampsize.13, proximity=TRUE, do.trace=TRUE) > rf Call: randomForest(x = data.frame(data2[, c(65, 69, 72, 43, 3)], factor(data2[, 63]), factor(data2[, 2]), factor(data2[, 14] > 0)), y = factor(data2[, 13]), sampsize = vector_for_sampsize.13, proximity = TRUE, do.trace = TRUE) Type of random forest: classification Number of trees: 500 No. of variables tried at each split: 2 OOB estimate of error rate: 50.53% Confusion matrix: 1 2 3 class.error 1 14 10 6 0.5333333 2 13 9 8 0.7000000 3 8 3 24 0.3142857 MDSplot(rf,factor(data2[,13]), pch=as.character(factor(data2[,13]))) varImpPlot(rf) Отличается только третья группа от первых двух. На графике восстановленных расстояний между случаями видно что группы скорее перетекают 1-2-3. Ведущие переменные разделения групп лечения это ЧСС до., Возраст, Время пережатия аорты1 и слабо Традиц.терапия. Если осложнения не преобразовывать в два уровня, то картина еще четче становится Код rf<-randomForest(data.frame(data2[,c( 65, 69, 72, 43, 3)], factor(data2[,63]), factor(data2[,2]) , data2[,14]), factor(data2[,13]), sampsize=vector_for_sampsize.13, proximity=TRUE, do.trace=TRUE) MDSplot(rf,factor(data2[,13]), pch=as.character(factor(data2[,13]))) > rf Call: randomForest(x = data.frame(data2[, c(65, 69, 72, 43, 3)], factor(data2[, 63]), factor(data2[, 2]), data2[, 14]), y = factor(data2[, 13]), sampsize = vector_for_sampsize.13, proximity = TRUE, do.trace = TRUE) Type of random forest: classification Number of trees: 500 No. of variables tried at each split: 2 OOB estimate of error rate: 45.26% Confusion matrix: 1 2 3 class.error 1 17 9 4 0.4333333 2 12 10 8 0.6666667 3 6 4 25 0.2857143 фактически группы две - 1 и 3, вторая размазана между ними.  |
|
|
 |
 |
 1.09.2012 - 22:22 1.09.2012 - 22:22
Сообщение
#58
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
фактически группы две - 1 и 3, вторая размазана между ними. [/quote] на мой взгляд- на графиках отражена реальная ситуация,и я поняля свою ошибку- вот почему 2 группа размазана- она получала разные препараты из одной группы(вот почему их и объединили)- и у одной части имелось снижение ЧСС от исходных данных, а у других нет. как же я так упустила то. |
|
|
 |
 |
 1.09.2012 - 22:26 1.09.2012 - 22:26
Сообщение
#59
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
Сообщение отредактировал Диана - 1.09.2012 - 22:28 |
|
|
 |
 |
 3.09.2012 - 18:18 3.09.2012 - 18:18
Сообщение
#60
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
там тоже что и на первом графике, просто три оси показано от mds. (ну и на нем когда осложнения не как фактор с двумя уровнями, а как степень тяжести).  |
|
|
 |
 |
 7.09.2012 - 20:00 7.09.2012 - 20:00
Сообщение
#61
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Для новых данных надо заново номера переменных собирать в анализ. А прямая переписка форумная что то более одного сообщения в день считает спамом.
 |
|
|
 |
 |
 10.09.2012 - 11:33 10.09.2012 - 11:33
Сообщение
#62
|
|
|
Группа: Пользователи Сообщений: 1091 Регистрация: 26.08.2010 Пользователь №: 22699 |
Для новых данных надо заново номера переменных собирать в анализ. А прямая переписка форумная что то более одного сообщения в день считает спамом. Код > str(data3[,c(2, 3, 4, 21, 23, 24:38, 45:50, 68,70, 74,77, 92:106, 109:110, 18, 19, 20)]) 'data.frame': 95 obs. of 50 variables: $ пол : Factor w/ 2 levels "жен","муж": 2 2 2 2 2 2 2 2 2 1 ... $ возраст : int 60 67 62 73 68 69 60 66 72 61 ... $ ИМТ..кг.м2 : num 29.1 22.1 29.4 26.1 27.6 23.8 33.8 32.3 23 40.6 ... $ стресс.ЭхоКГ : int NA 1 1 1 0 1 0 1 0 0 ... $ X.1 : int NA 22 22 20 16 20 16 20 16 16 ... $ ИНЛС.ЛЖ : num NA 1.38 1.38 1.25 1 ... $ ГБ : int 3 3 3 3 3 3 3 3 3 3 ... $ ГЛЖ.new : int 1 1 1 0 0 0 1 1 1 1 ... $ ГБ.ГЛЖ : int 1 1 1 0 0 0 1 1 1 1 ... $ ИБС..стенокардия : int 2 1 2 2 2 3 2 2 0 2 ... $ постинф.кардиоскл : int 1 1 1 1 0 1 1 1 0 0 ... $ НК..фк : int 2 2 2 2 2 2 2 2 1 2 ... $ ДЛП : int 0 1 1 1 1 0 1 1 1 1 ... $ размер.АБА : int 2 2 1 1 2 3 3 1 3 1 ... $ синдромность : int 1 3 3 3 3 1 3 1 3 1 ... $ прех.ишем.послеопер : int 1 1 0 0 0 1 1 0 0 1 ... $ прех.ишем.послеопер.1 : int 1 1 0 0 0 2 1 0 0 1 ... $ доступ : int 1 2 1 1 1 2 2 2 1 1 ... $ курение : int 0 1 1 1 1 1 1 0 1 0 ... $ диаст..Дисфункция00 : int 0 0 1 1 1 0 0 0 1 0 ... $ САД.д.о : int 140 130 130 120 130 120 120 120 120 120 ... $ ДАД.д.о : int 80 80 80 80 80 80 80 80 80 70 ... $ ЧСС.д.о : int 72 62 60 64 68 64 68 60 58 56 ... $ САД.п.о : int 130 140 120 130 120 85 120 145 140 130 ... $ ДАД.п.о : int 80 80 80 80 80 40 70 80 80 80 ... $ ЧСС.п.о : int 80 60 78 78 86 72 80 82 80 82 ... $ операция1 : int 1 1 1 1 1 1 1 1 1 4 ... $ время.операции1 : int 170 130 120 115 175 215 220 220 110 240 ... $ время.переж.аорты1 : int 43 41 25 30 55 28 40 53 40 48 ... $ кровопотеря1 : int 800 500 450 300 350 1200 500 700 200 700 ... $ ГЛЖ.new.1 : num 5.9 1 1 0 0 0 1 1 1 1 ... $ зоны.гипо.и.акин00 : num 4.4 1 1 0 0 1 0 0 0 0 ... $ КДР..см00 : num 174 4.3 5.7 4.4 4.8 4.8 5.2 4 5.2 5.3 ... $ КСР..см00 : num 85 3.2 3.9 2.5 3.1 3.4 3.6 2.8 3.4 3.2 ... $ КДО..мл00 : int 88 83 160 88 108 108 130 70 130 135 ... $ индекс.КДО..00 : num 43 51.9 76.5 45.4 58 58.5 61.8 32.7 75.4 68.5 ... $ КСО00 : int 49 41 66 22 38 47 54 30 47 41 ... $ инд.КСО00 : num 86 25.6 31.5 11.3 20.4 25.4 25.7 14 27.3 20.8 ... $ ФВ00 : num 1.4 51 59 75 65 50 58 57 64 60 ... $ УО00 : num 1.2 42 94 66 70 61 76 40 83 94 ... $ ТМЖП00 : num 0.44 1.2 1.2 0.9 1.1 0.9 1.3 1.5 1 1.3 ... $ ТЗСТ.ЛЖ00 : num 411.5 1.1 1 1 1.1 ... $ ОТС.ЛЖ : num 205.8 0.53 0.39 0.43 0.46 ... $ ММ.ЛЖ.формула.Devereux: num 3.2 202.8 306.6 157.9 228.2 ... $ ИММ.ЛЖ : num 5 127 146 79 120 ... $ d.аорты00 : num 1 3.2 3.5 3.2 3.4 3.8 3.7 3.8 3.6 3.2 ... $ диаст..Дисфункция00.1 : int 3 0 1 1 1 0 0 0 1 0 ... $ п.о.кард.осложн : int 0 0 0 0 0 1 0 0 0 2 ... $ Кард.осл.я : int 0 0 0 0 0 1 0 0 0 1 ... $ летальность : int 0 0 0 0 0 0 0 0 0 0 ... > nrow(na.omit(data3[,c(2, 3, 4, 21, 23, 24:38, 45:50, 68,70, 74,77, 92:106, 109:110, 18, 19, 20)])) [1] 79 > nrow((data3[,c(2, 3, 4, 21, 23, 24:38, 45:50, 68,70, 74,77, 92:106, 109:110, 18, 19, 20)])) [1] 95 что из перечисленного точно в шкале наименований измерено?  |
|
|
 |
 |
 10.09.2012 - 21:47 10.09.2012 - 21:47
Сообщение
#63
|
|
|
Группа: Пользователи Сообщений: 39 Регистрация: 30.06.2012 Пользователь №: 23898 |
ГБ : int 3 3 3 3 3 3 3 3 3 3 ...
$ ГЛЖ.new : int 1 1 1 0 0 0 1 1 1 1 ... $ ГБ.ГЛЖ : int 1 1 1 0 0 0 1 1 1 1 ... $ ИБС..стенокардия : int 2 1 2 2 2 3 2 2 0 2 ... $ постинф.кардиоскл : int 1 1 1 1 0 1 1 1 0 0 ... $ НК..фк : int 2 2 2 2 2 2 2 2 1 2 ... $ ДЛП : int 0 1 1 1 1 0 1 1 1 1 ... $ размер.АБА : int 2 2 1 1 2 3 3 1 3 1 ... $ синдромность : int 1 3 3 3 3 1 3 1 3 1 ... $ прех.ишем.послеопер : int 1 1 0 0 0 1 1 0 0 1 ... $ прех.ишем.послеопер.1 : int 1 1 0 0 0 2 1 0 0 1 ... $ доступ : int 1 2 1 1 1 2 2 2 1 1 ... $ курение : int 0 1 1 1 1 1 1 0 1 0 ... $ диаст..Дисфункция00 : int 0 0 1 1 1 0 0 0 1 0 ... |
|
|
 |
 |
  |